Mối liên quan giữa tính đa hình của hệ gene và khả năng mẫn cảm với bệnh
1) Genome của loài người có những biến thể di truyền khác nhau và điểm đó làm nên sự khác nhau giữa người này với người kia. Phần lớn trong số những biến thể đó là hàng triệu các điểm đa hình tại những vị trí nucleotide nhất định đã làm thay đổi mã di truyền. Những điểm khác biệt đó được gọi là những điểm đa hình đơn nucleotide (single nucleotide polymorphisms, SNPs (đọc là sờ-níp)) hiện đang được Dự án quốc tế HapMap tiến hành thống kê một cách hệ thống (1). Về mặt tiến hóa, những điểm khác biệt này được giả thuyết là các dạng đột biến trung tính tạo nên sự đa dạng về mặt di truyền giữa các cá thể loài người. Tuy nhiên, một số điểm đa hình SNP có thể liên quan đến khả năng mẫn cảm với bệnh.
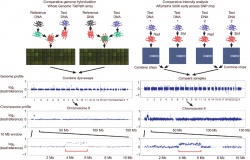
2) So với các điểm đa hình đơn nucleotide, các biến dị khác biệt về số lượng bản sao có tần số xuất hiện thấp hơn nhiều. Đây là những đột biến thêm hoặc mất một đoạn nhiễm sắc thể (NST) làm thay đổi số lượng bản sao của mỗi gene, thay vì là hai allele như bình thường (2). Một số nghiên cứu mô tả mức độ phỏ biến của các điểm đa hình dạng này trên hệ gene người (3, 4). Công trình mới đây (5) tiến hành khảo sát các biến thể đa hình số bản sao (copy-number variants, CNVs) trên toàn bộ hệ gene người từ hàng trăm mẫu đối chiếu của 4 quần thể người. Các nhà nghiên cứu đã thống kê khoảng 1500 vùng biến đổi mang CNV (chiếm 12% genome) chứa hàng trăm gene cấu trúc hoặc các vùng chức năng khác. Kết quả này cho thấy nguồn đa dạng di truyền của loài người không chỉ dựa vào hàng triệu điểm SNP mà còn cả ở biến dị thêm hay mất những đoạn NST. Vấn đề đặt ra hiện nay là làm thế nào xác định chính xác đặc điểm của một hệ gene "bình thường" của con người.
3) Để dò tìm các CNV, nhóm Redon và cộng sự (5) đã sử dụng 2 công nghệ genomics bổ trợ cho nhau. Kỹ thuật thứ nhất sử dụng định hướng xác định kiểu gene (genotyping) nhắm sàng lọc khoảng 500,000 SNP để tìm kiếm những chuỗi SNP kế cận có tỷ lệ khác thường so với 2 mô hình (gọi là allele) lý thuyết của từng SNP. Kỹ thuật thứ hai là so sánh từng mẫu với mẫu chuẩn và tìm kiếm các điểm khác biệt một cách hệ thống của hơn 26,000 đoạn nhiễm sắc thể lớn mà tổng chiều dài đã chiếm gần như tất cả phần hệ gene đã được xử lý trình tự hiện nay. Việc kết hợp hai hướng tiếp cận này có thể cho phép dò tìm gần như tất cả các kiểu CNV. Kết quả là nhóm tác giả đã phát hiện 1447 CNV trong số 270 mẫu HapMap. Chiều dài ước tính trung bình của các vùng chứa CNV trong mỗi hệ gene là vào khoảng 20 triệu cặp base. Con số này lớn gấp 5 đến 10 lần những lượng nucleotide đa hình SNP tìm thấy từ 2 hệ gene ngẫu nhiên ở các nghiên cứu trước kia. Hơn một nửa số CNV được xác định là vùng chứa những gene cấu trúc đã được danh định trên genome. Do đó, người ta tin rằng CNV đóng vai trò quan trọng trong việc hình thành bệnh di truyền phức tạp có nguyên nhân do tương tác nhiều gene hoặc tương tác giữa gene và môi trường.
4) Các đa hình về số lượng bản sao (CNV) bằng cách nào có thể quyết định đến những bệnh di truyền phức tạp? Khi xảy ra những đột biến thêm hoặc mất đi một đoạn nucleotide có chứa gene hoặc vùng điều hòa gene, người bệnh có nhiều khả năng sẽ bị mất cân bằng về lượng RNA và protein thích hợp do gene đó mã hóa. Đối với những gene hoặc con đường trao đổi chất mà số lượng enzyme chức năng đóng vai trò chủ chốt thì đột biến CNV có thể gây nên những biến đổi về tính mẫn cảm đối với bệnh tật. Một ví dụ điển hình, những sai khác về lượng bản sao của gene globin có liên quan điều nhiều dạng bệnh di truyền haemoglobin ví dụ như bệnh alpha-thalassaemias (6). Gần đây, số lượng bản sao khác nhau của gene CCL3L1 cũng cho thấy làm tăng khả năng kháng lại sự xâm nhiễm của HIV (7).
Tài liệu tham khảo[sửa]
- International HapMap Consortium Nature 437, 1299-1320 (2005).
- Feuk, L. et al. Nature Rev. Genet. 7, 85-97 (2006).
- Hinds, D. A. et al. Nature Genet. 38, 82-85 (2005).
- McCarroll, S. A. et al. Nature Genet. 38, 86-92 (2005).
- Redon, R. et al. Nature 444, 444-454 (2006).
- Weatherall, D. J. Am. J. Hum. Genet. 74, 385–392 (2004).
- Gonzalez, E. et al. Science 307, 1434–1440 (2005).